Single cell RNA-Seq
Ofrecemos el análisis bioinformático de datos NGS para células individuales
Home / Single cell RNA-Seq
Estudio de la expresión génica a nivel celular
El análisis Single cell RNA-Seq permite analizar el transcriptoma de cada célula de manera individual y puede revelar procesos biológicos y mecanismos moleculares específicos que podrían no ser detectados mediante técnicas de secuenciación de ARN a nivel poblacional o de tejido.
El análisis bioinformático que llevamos a cabo en Dreamgenics incluye:
- Control de calidad de la secuenciación y mapeado.
- Alineamiento de lecturas frente a genoma de referencia.
- Cuantificación de la expresión génica a nivel de célula única.
- Filtrado de células atendiendo a criterios de calidad.
- Integración de múltiples réplicas biológicas.
- Reducción de la dimensionalidad de los datos.
- Clustering o división de las células en distintos grupos.
- Anotación de tipo celular y validación mediante genes marcadores.
- Identificación de marcadores de clúster.
- Estudio del patrón evolutivo o de maduración celular (Análisis de Velocidad y/o Trayectoria).
- Estudio de comunicación intercelular.
- Estudio comparativo mediante identificación de marcadores conservados, análisis composicional, análisis de expresión diferencial de tipo “Pseudobulk” y análisis de enriquecimiento en rutas y ontologías génicas.

Servicios Bioinformáticos
Conoce más información sobre nuestros servicios de análisis de datos NGS descargando el folleto
Resultados en Genome One Reports
Los resultados de todos los análisis dan lugar a gráficos interactivos que se pueden explorar en nuestra plataforma Genome One Reports y descargarse en PDF para su uso en publicaciones científicas.
- Tendrás acceso al análisis de calidad de las secuencias obtenidas
- Tendrás acceso a los resultados del análisis de Cell Ranger
- Gráficos PCA plot, Cell Clustering, Trajectory Analisis, RNA Velocity, Cell Chat, etc. en función del paquete elegido
- Informes individuales para cada condición experimental y para cada análisis comparativo
- Todas las tablas y figuras son fácilmente exportables, listas para ser utilizadas en publicaciones científicas
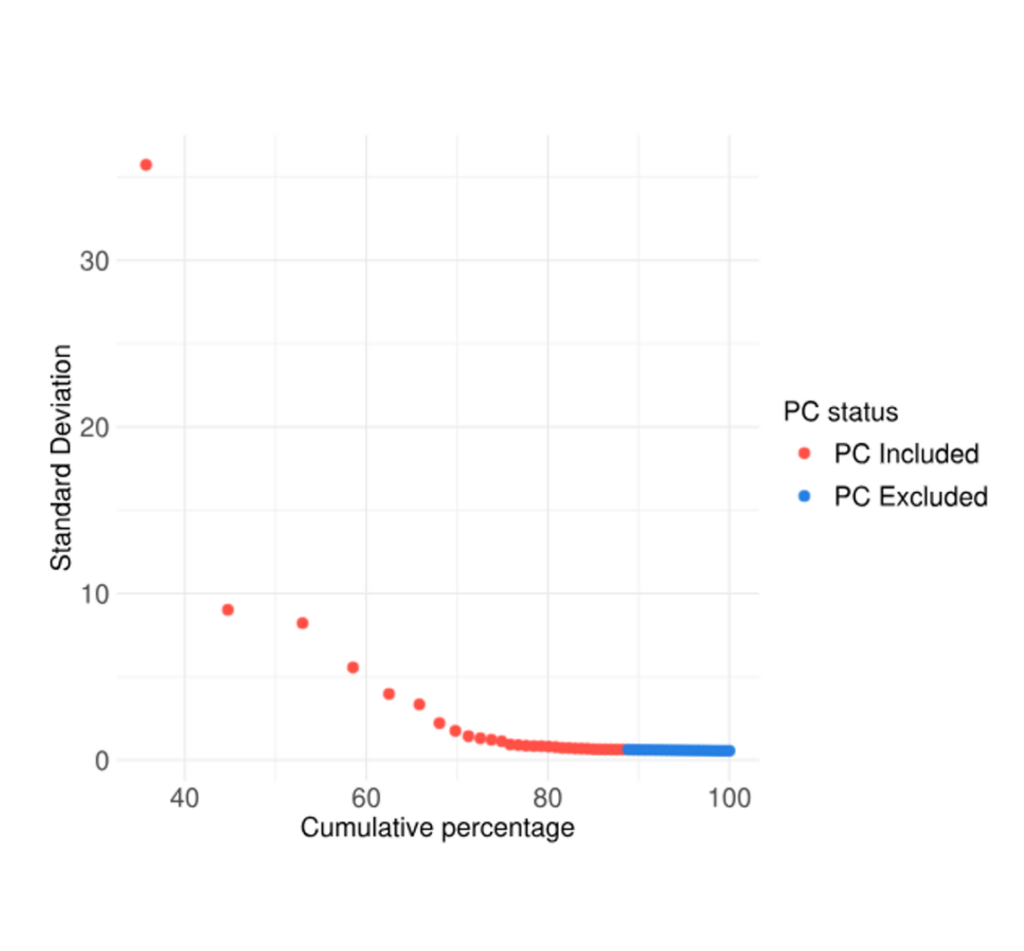
PCA Plot
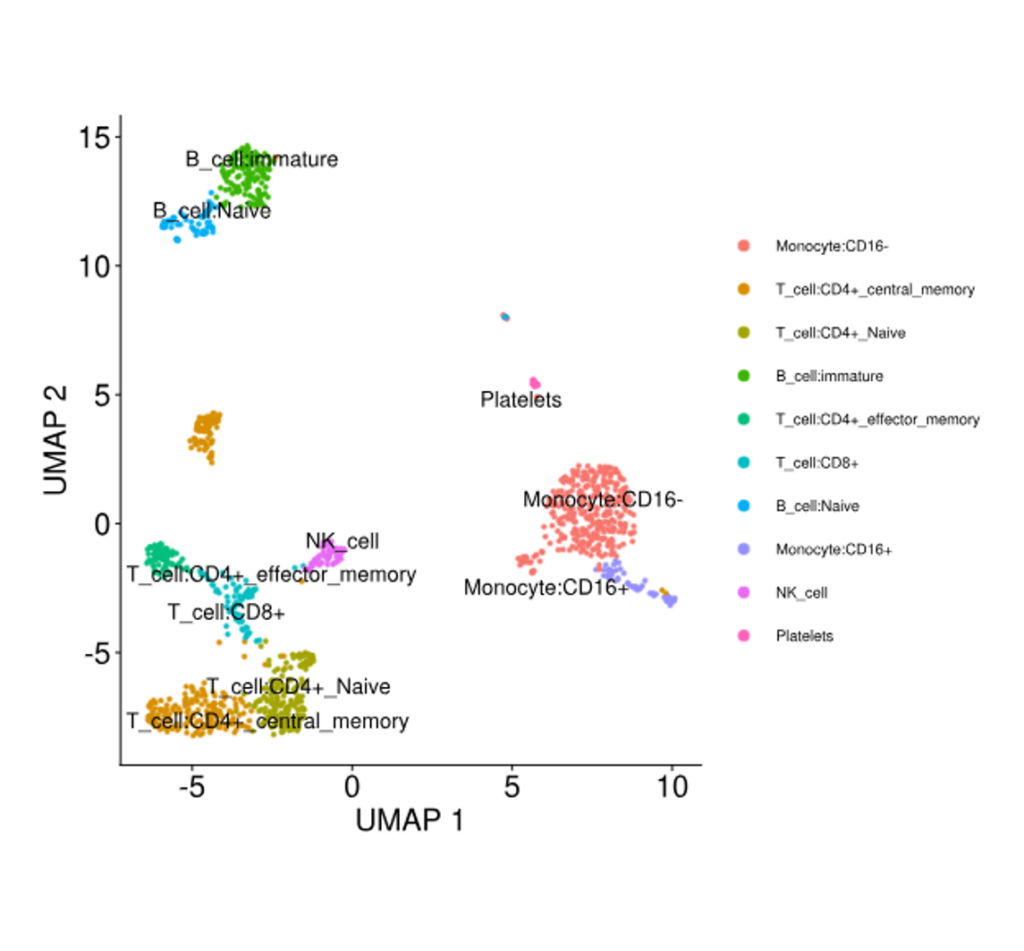
Cell Clustering
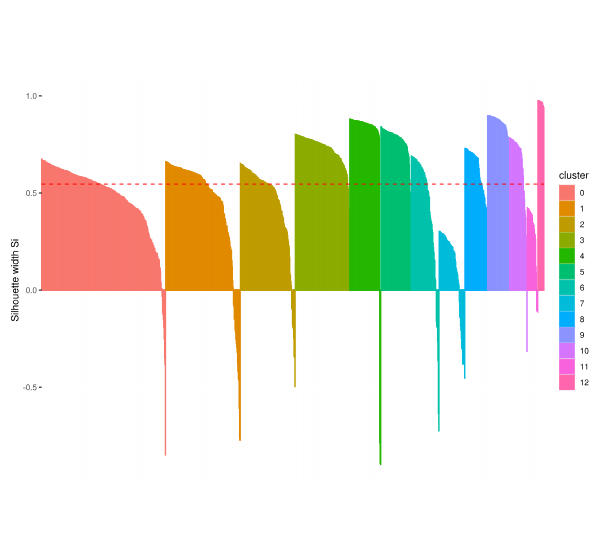
Cluster Evaluation
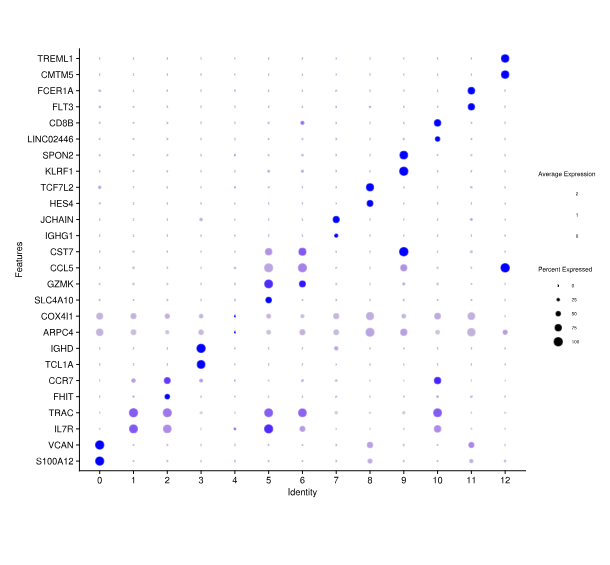
Differentially Expressed Genes
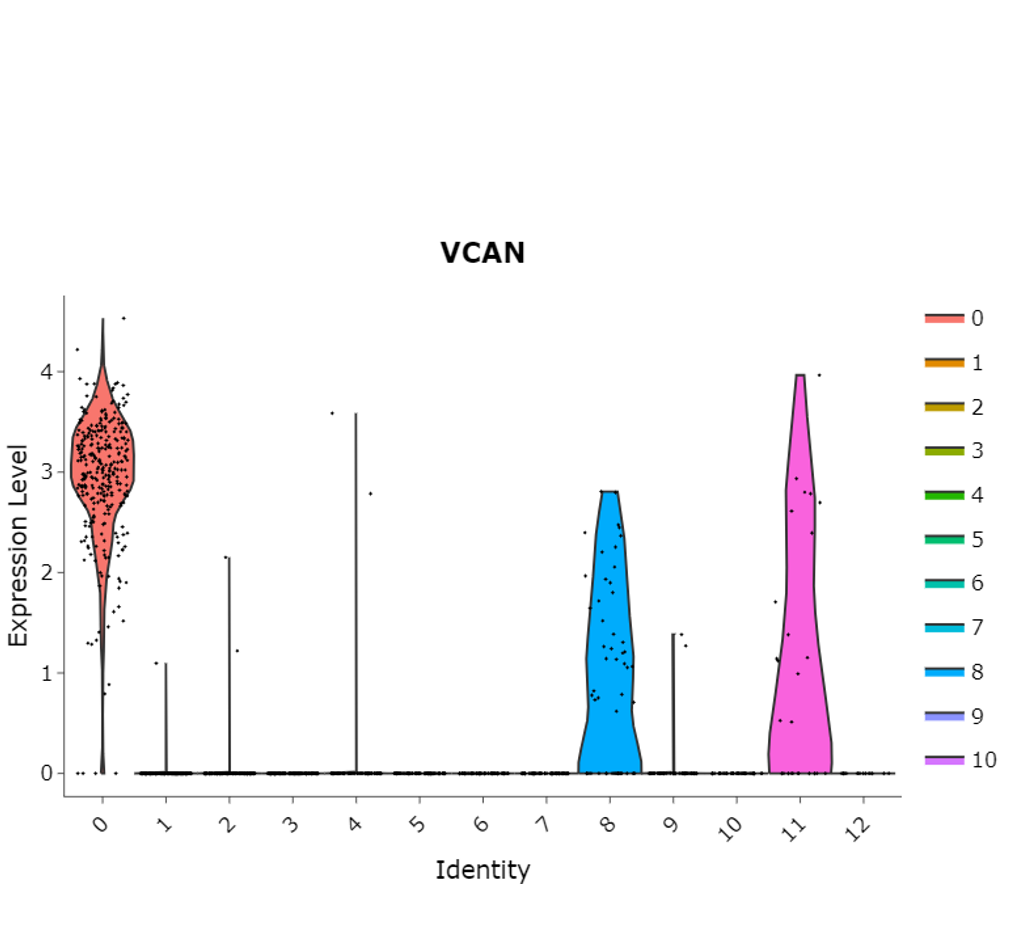
Violin Plot
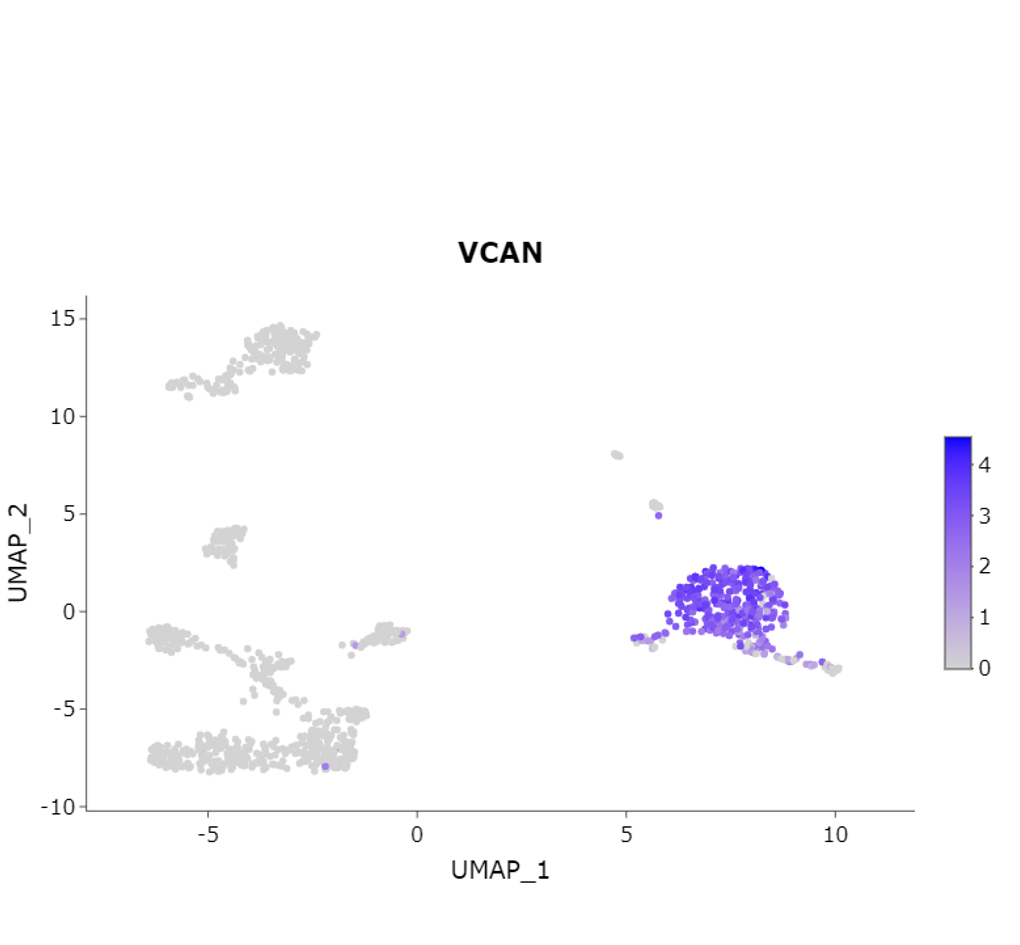
Feature Plot

Differentially Expressed Genes

Violin Plot

Feature Plot
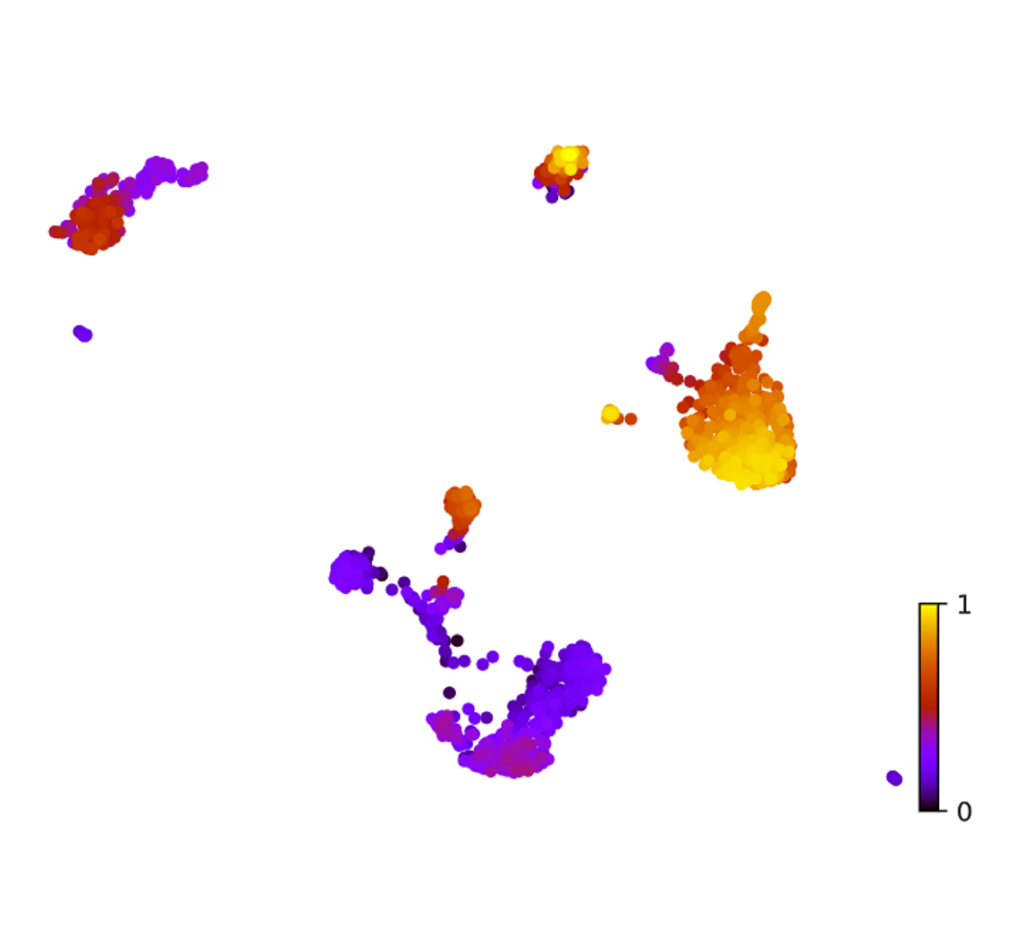
RNA Velocity
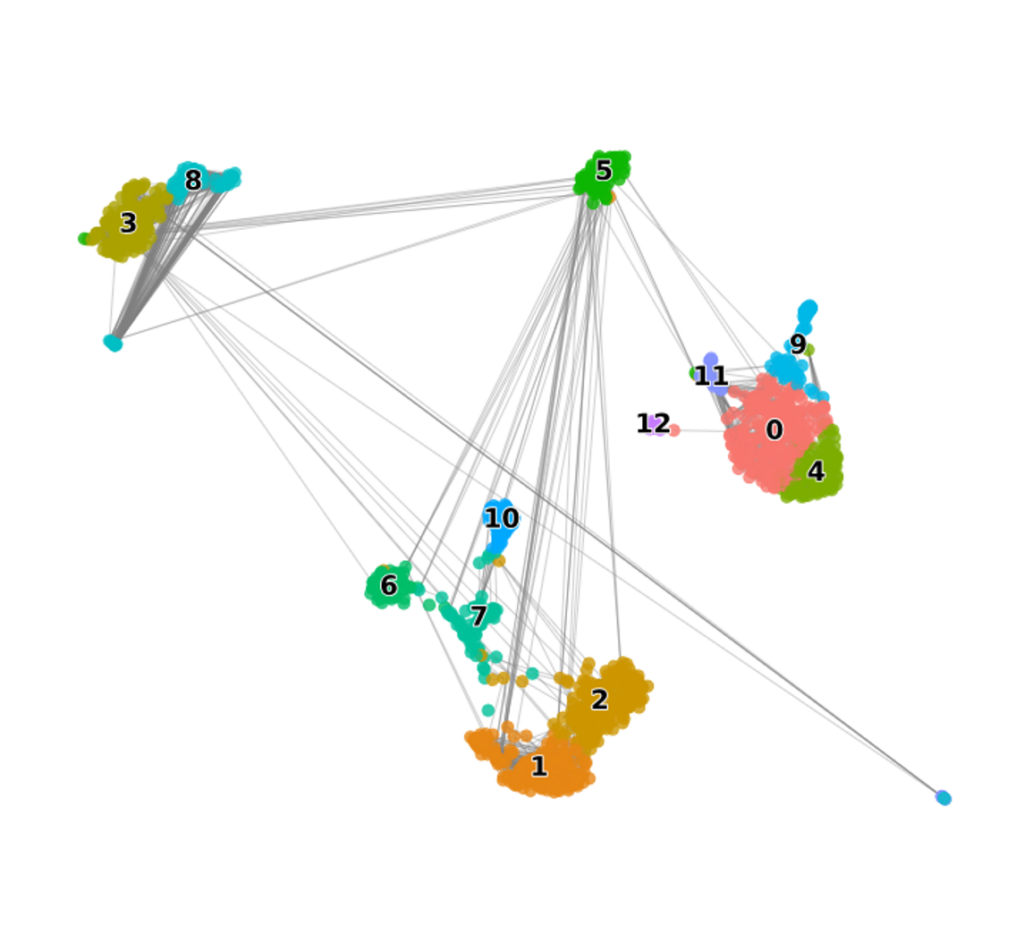
Neighbor Graph
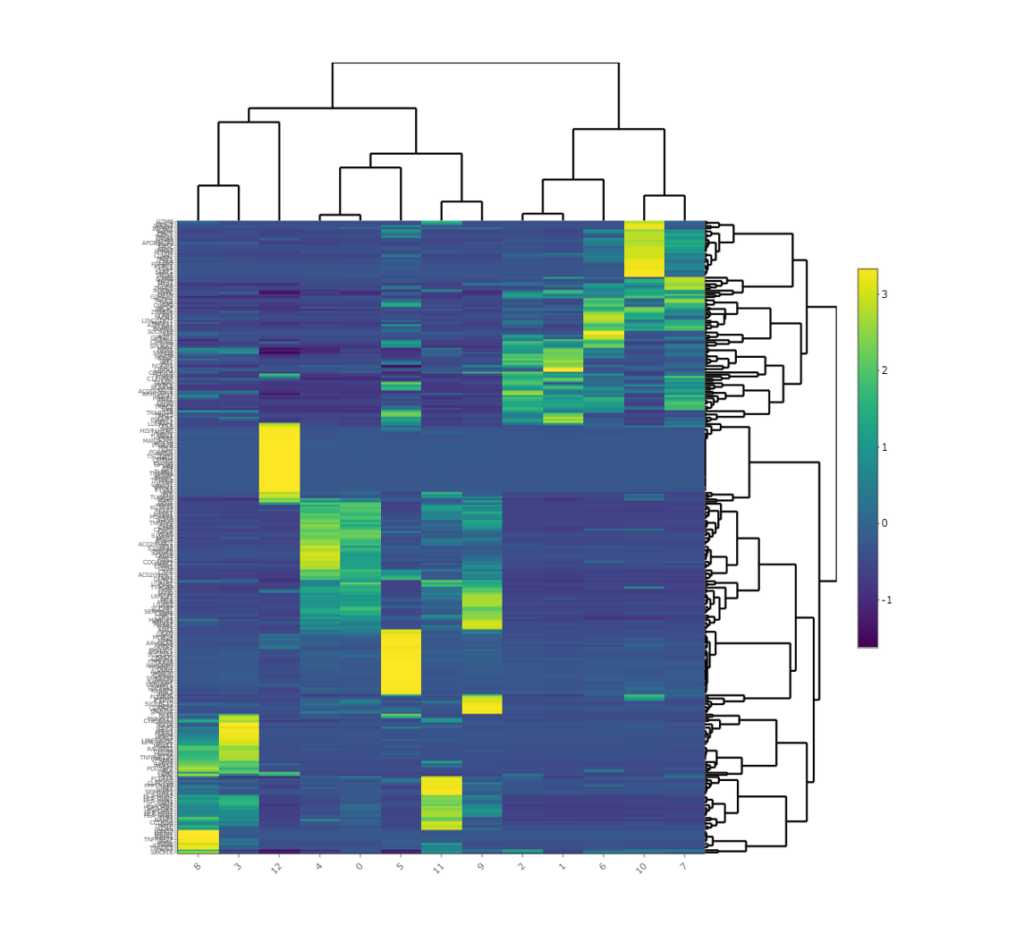
Heatmap
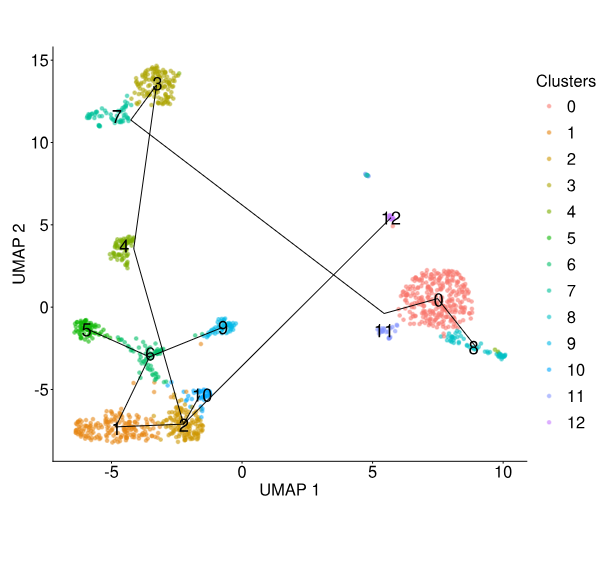
Trajectory Analysis
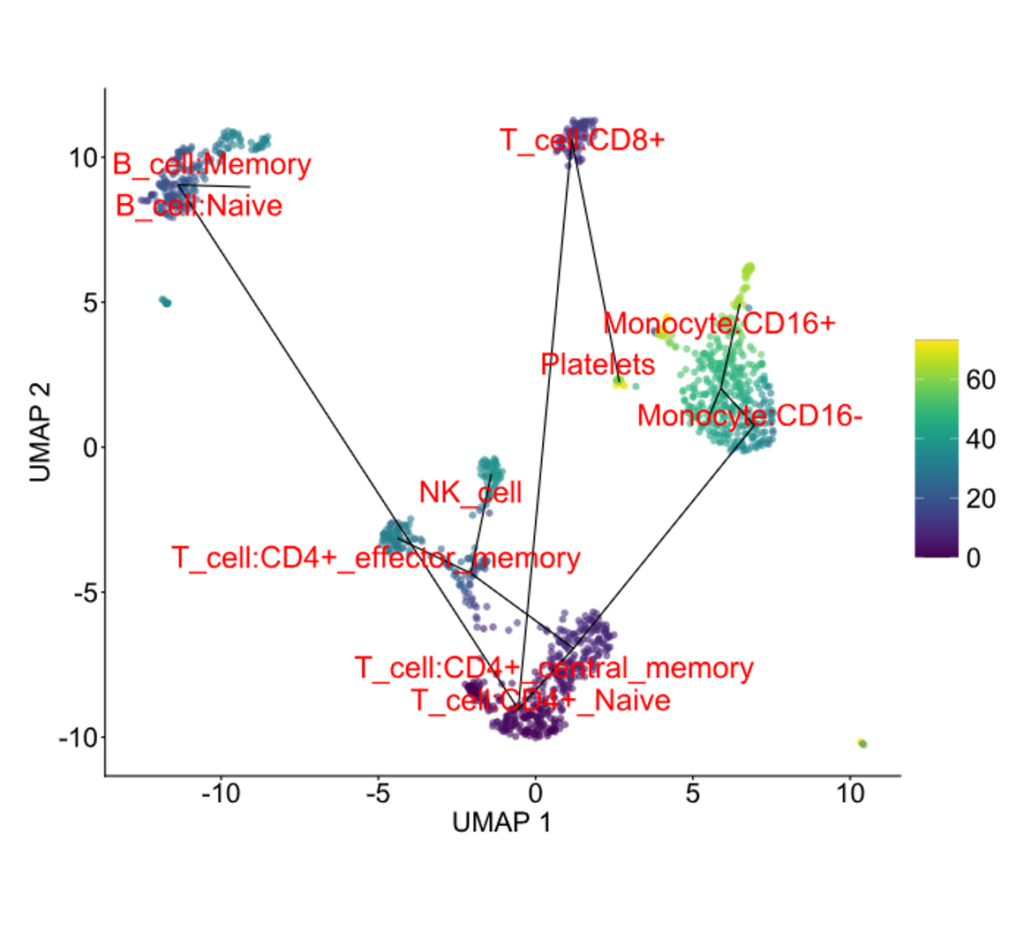
Pseudotime trajectory
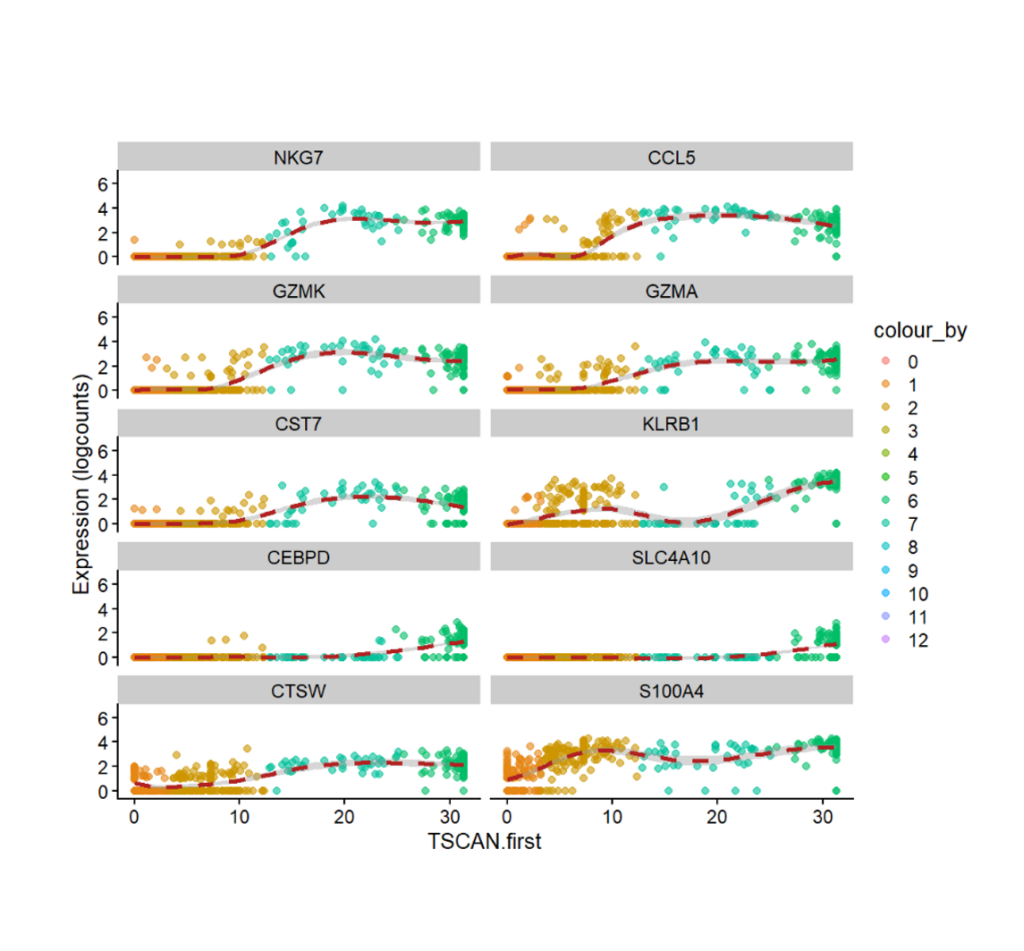
TOP 10 Expressed Genes (Up & Down) in a trajectory line
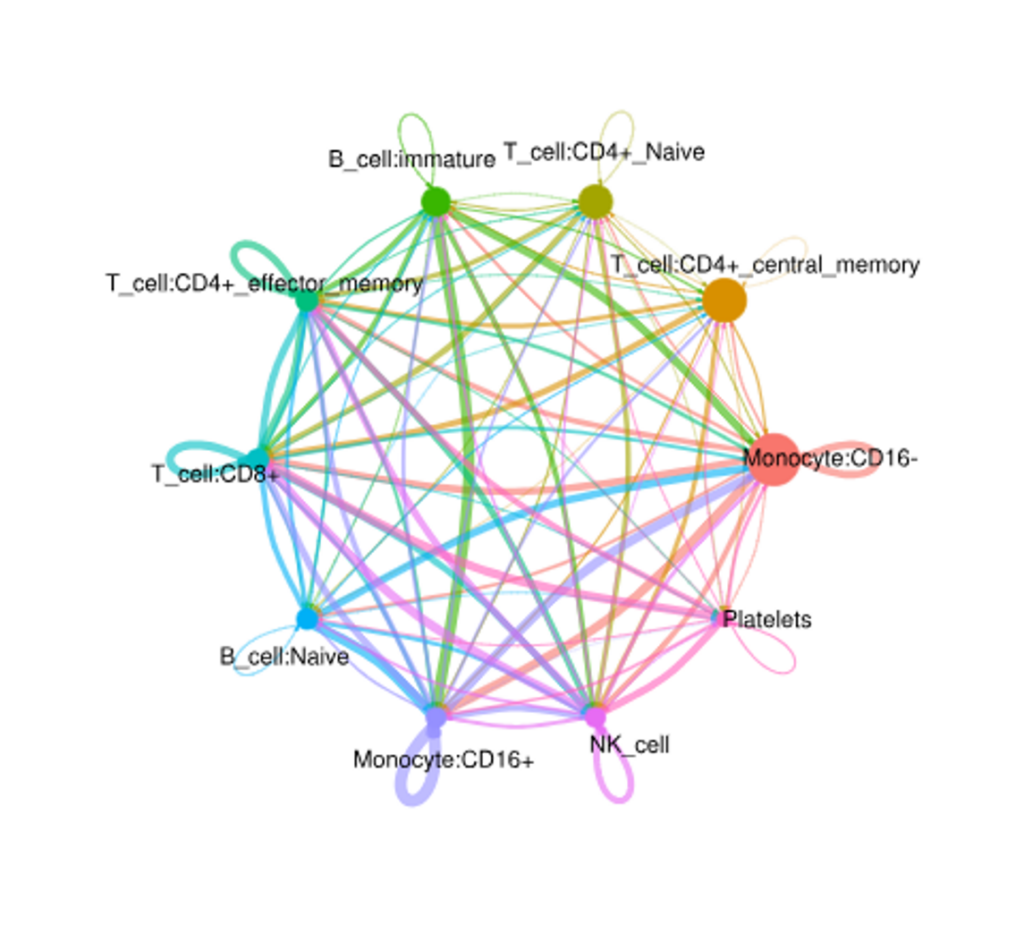
Cell chat
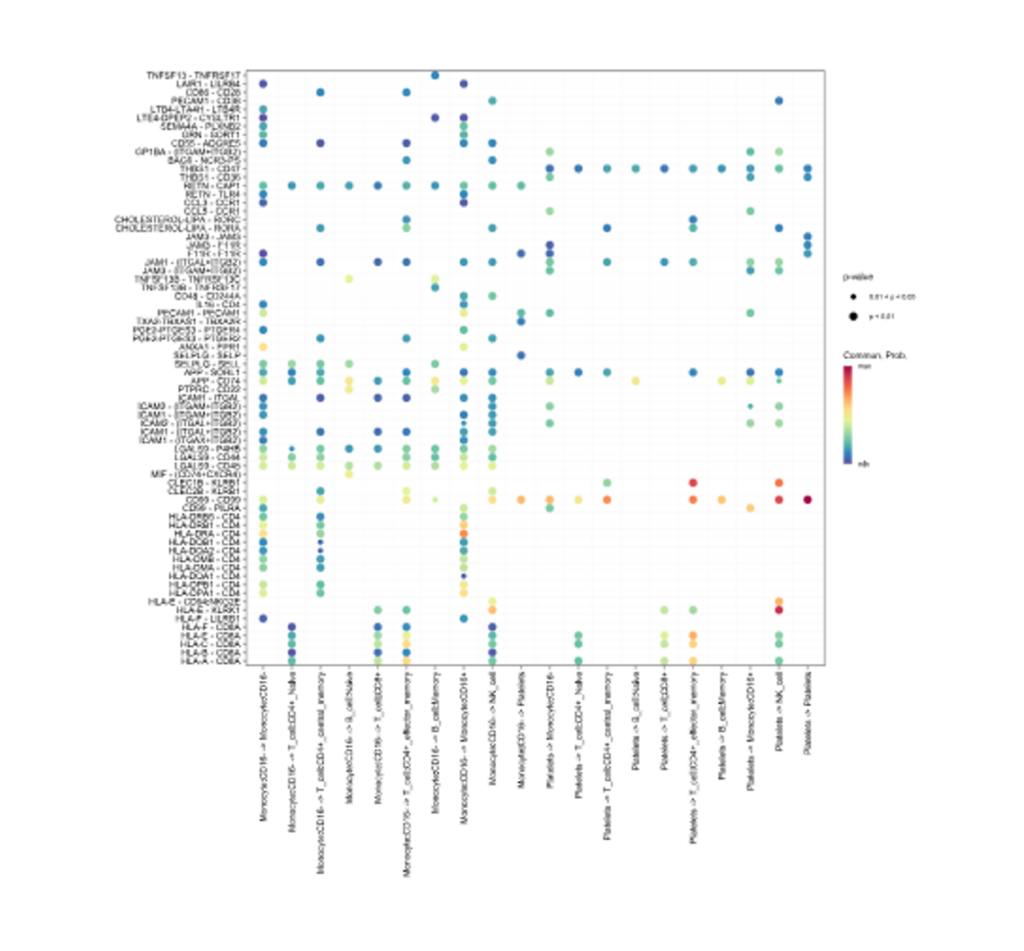
Heatmap cell chat
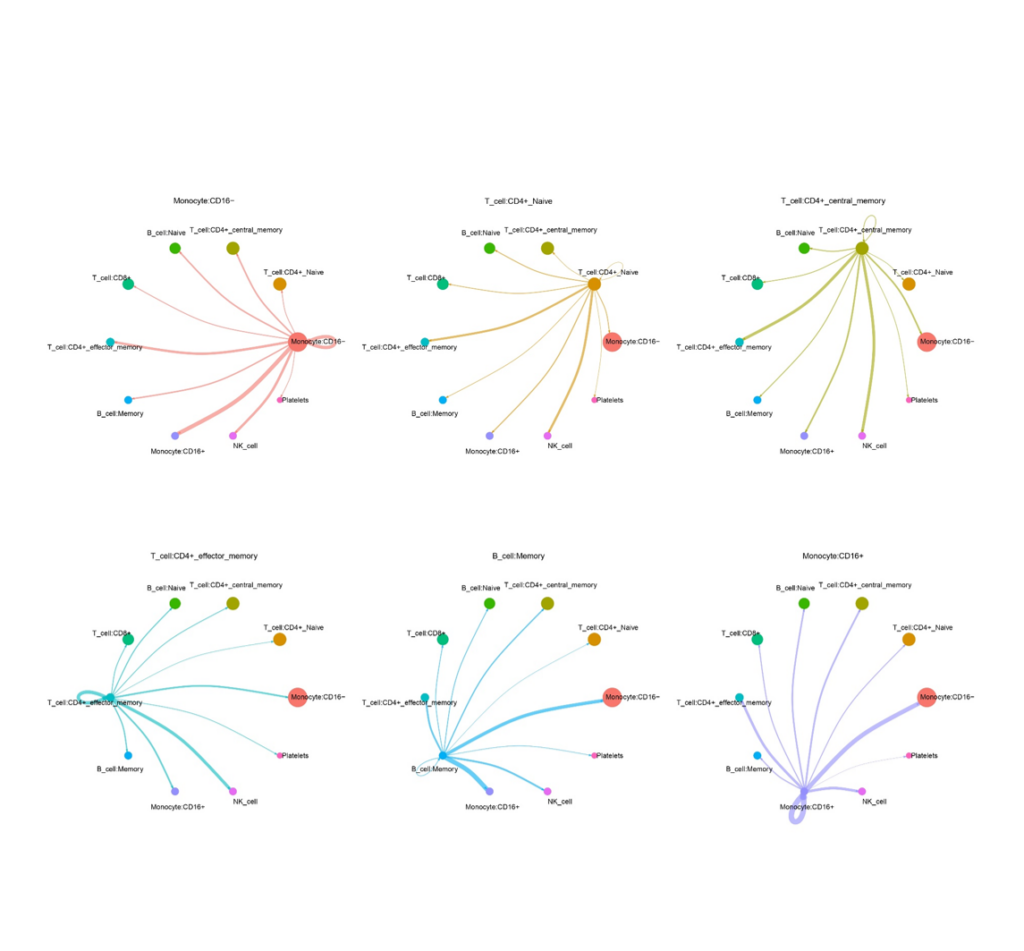
Principal Conections Between Cells
Opciones disponibles
Nos adaptamos a las necesidades de cada cliente a través de dos paquetes de análisis y la posibilidad de realizar un análisis completamente personalizado.
Paquete estándar
- Análisis de calidad
- Integración de múltiples muestras
- Reducción de la dimensionalidad
- Cell Clustering (2D & 3D)
- Anotación de tipo celular
- Identificación de marcadores de clúster
- Análisis de Velocidad
- Resultados en Genome One Reports
Paquete ampliado
- Todo lo incluído en el paquete estándar
- Análisis de trayectoria
- Análisis de comunicación intercelular
- Resultados en Genome One Reports
"La tecnología Single cell RNA-seq nos permite desarrollar enfoques más precisos para estudiar procesos fisiológicos y patológicos a nivel de célula única, facilitando la identificación de nuevos biomarcadores y abriendo nuevas vías de investigación en las enfermedades con las que trabajamos.”

Dra. Elena Sánchez Luis
Investigadora

























